در ده سال گذشته، فناوری ویرایش ژن مبتنی بر CRISPR به سرعت توسعه یافته است و با موفقیت در درمان بیماریهای ژنتیکی و سرطان در آزمایشهای بالینی انسانی به کار گرفته شده است.در همان زمان، دانشمندان در سراسر جهان به طور مداوم از ابزارهای جدید جدید با پتانسیل ویرایش ژن برای حل مشکلات ابزارهای ویرایش ژن موجود و ابزارهای تعیین کننده استفاده می کنند.
در سپتامبر 2021، تیم ژانگ فنگ مقالهای را در مجله Science [1] منتشر کرد و دریافت که طیف وسیعی از ترانپوسترها آنزیمهای اسید نوکلئیک هدایتکننده RNA را رمزگذاری کرده و نام آن را سیستم امگا (از جمله ISCB، ISRB، TNP8) گذاشتند.این مطالعه همچنین نشان داد که سیستم امگا از بخشی از RNA برای هدایت زنجیره دوگانه DNA برش، یعنی ωRNA استفاده می کند.مهمتر از آن، این آنزیمهای اسید نوکلئیک بسیار کوچک هستند و فقط 30 درصد از CAS9 را تشکیل میدهند، که به این معنی است که احتمال انتقال آنها به سلولها بیشتر است.

در 12 اکتبر 2022، تیم ژانگ فنگ در مجله Nature با عنوان: ساختار Omega Nickase ISRB in Complex with ωrna and Target DNA [2] منتشر کرد.
این مطالعه بیشتر ساختار میکروسکوپ الکترونی منجمد ISRB-orRNA و مجموعه DNA هدف را در سیستم امگا تجزیه و تحلیل کرد.
ISCB جد CAS9 است، و ISRB همان شیء عدم وجود دامنه اسید نوکلئیک HNH در ISCB است، بنابراین اندازه کوچکتر است، فقط حدود 350 اسید آمینه.DNA همچنین پایه و اساس توسعه بیشتر و تحول مهندسی را فراهم می کند.

IsrB با هدایت RNA یکی از اعضای خانواده OMEGA است که توسط ابرخانواده ترانسپوزون های IS200/IS605 کدگذاری شده است.از تجزیه و تحلیل فیلوژنتیک و حوزه های منحصر به فرد مشترک، IsrB احتمالاً پیشرو IscB است که جد Cas9 است.
در می 2022، آزمایشگاه اژدهای دوستداشتنی دانشگاه کرنل مقالهای را در مجله Science [3] منتشر کرد که در آن ساختار IscB-ωρNA و مکانیسم برش DNA آن را تحلیل میکرد.

در مقایسه با IscB و Cas9، IsrB فاقد دامنه نوکلئاز HNH، لوب REC و بیشتر حوزههای متقابل توالی PAM است، بنابراین IsrB بسیار کوچکتر از Cas9 است (فقط حدود 350 اسید آمینه).با این حال، اندازه کوچک IsrB توسط یک RNA راهنمای نسبتا بزرگ متعادل می شود (امگا RNA آن حدود 300 nt طول دارد).
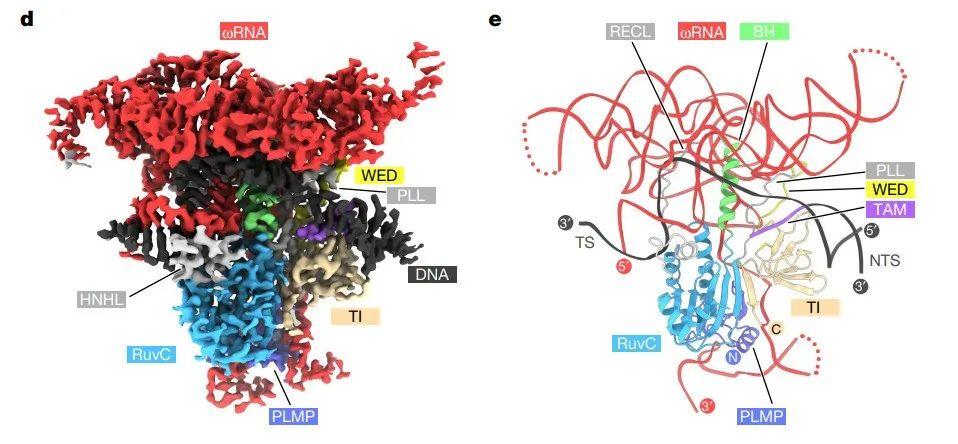
تیم ژانگ فنگ ساختار میکروسکوپ انجمادی الکترونی IsrB (DtIsrB) را از باکتری بی هوازی با گرمای مرطوب Desulfovirgula thermocuniculi و مجموعه ORNA و DNA هدف آن تجزیه و تحلیل کرد.تجزیه و تحلیل ساختاری نشان داد که ساختار کلی پروتئین IsrB دارای ساختار ستون فقرات با پروتئین Cas9 است.
اما تفاوت این است که Cas9 از لوب REC برای تسهیل تشخیص هدف استفاده می کند، در حالی که IsrB به ωRNA خود متکی است، بخشی از آن ساختار سه بعدی پیچیده ای را تشکیل می دهد که مانند REC عمل می کند.
برای درک بهتر تغییرات ساختاری IsrB و Cas9 در طول تکامل از RuvC، تیم ژانگ فنگ ساختارهای اتصال DNA هدف RuvC (TtRuvC)، IsrB، CjCas9 و SpCas9 را از Thermus thermophilus مقایسه کردند.
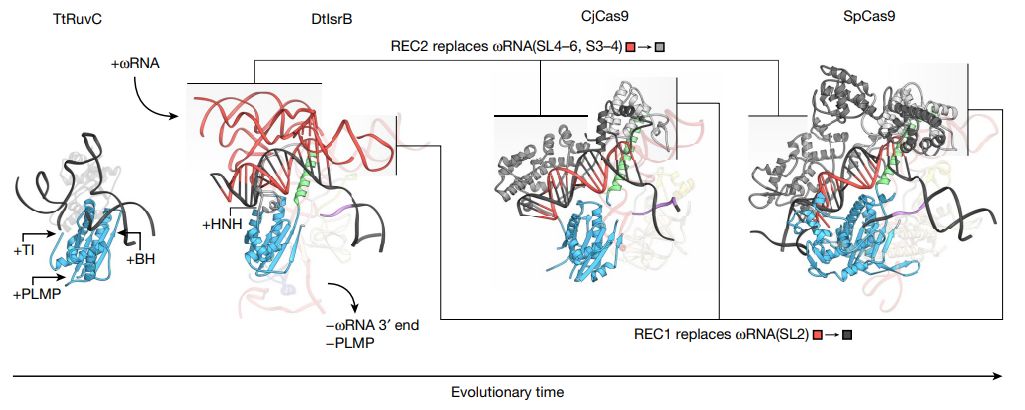
تجزیه و تحلیل ساختاری IsrB و ωRNA آن روشن میکند که چگونه IsrB-ωRNA به طور مشترک DNA هدف را تشخیص داده و میشکند، و همچنین مبنایی برای توسعه و مهندسی بیشتر این هسته کوچکسازی شده فراهم میکند.مقایسه با سایر سیستمهای هدایتشونده RNA، برهمکنشهای عملکردی بین پروتئینها و RNAها را برجسته میکند و درک ما از زیستشناسی و تکامل این سیستمهای متنوع را ارتقا میدهد.
پیوندها:
1.https://www.science.org/doi/10.1126/science.abj6856
2.https://www.science.org/doi/10.1126/science.abq7220
3.https://www.nature.com/articles/s41586-022-05324-6
زمان ارسال: اکتبر-14-2022








